1074 - USO DE MODELOS PRONÓSTICOS BASADOS EN INTELIGENCIA ARTIFICIAL PARA LA EVALUACIÓN DEL RIESGO DE BACTERIEMIAS POR BACILOS GRAM NEGATIVOS MULTIRRESISTENTES
1Hospital General Universitario José María Morales Meseguer, Murcia, España. 2Universidad Internacional de La Rioja, Logroño, España.
Objetivos: Desarrollar y validar modelos predictivos basados en inteligencia artificial que permitan la identificación temprana de pacientes con alto riesgo de presentar bacteriemia por bacilos Gram negativos (BGN) multirresistentes.
Métodos: Se realizó un estudio retrospectivo basado en un registro existente de pacientes diagnosticados con bacteriemia por BGN entre el 1 de enero de 2018 y el 31 de agosto de 2023. Se utilizaron las recomendaciones de la European Society of Clinical Microbiology and Infectious Diseases (ESCMID) para establecer la definición de BGN multirresistente. El análisis de los datos se centró en variables sociodemográficas, antecedentes médicos, factores relacionados con la atención sanitaria, estado inmunitario, foco de infección y factores pronósticos. El estudio evaluó los modelos de análisis mediante red neuronal, árbol de decisión, random forest y gradient boost machine.
Resultados: Se incluyeron 1.051 pacientes con bacteriemia por BGN en el estudio, de los cuales 80 (7,6%) tuvieron aislamiento de un BGN multirresistente. En la tabla se pueden consultar las características demográficas, clínicas, microbiológicas y pronósticas de los pacientes. El modelo random forest demostró un notable rendimiento predictivo con una sensibilidad del 87%, una especificidad del 68% y una precisión de entrenamiento global del 67,5 ± 3,2%, con un área bajo la curva de 0,82 ROC (Receiver Operating Characteristic), la cual se muestra en la figura. En cuanto a factores predictores de multirresistencia, el modelo encontró mayor significación para el centro de salud, el uso previo de antibióticos, el lugar de la infección y la edad. Por último, respecto al pronóstico de los pacientes, se encontró una tendencia a mayor estancia media en el grupo de BGN multirresistentes (14,5 ± 18,2 días vs. 11,6 ± 12,3 días, p = 0,062), con diferencias significativas en la incidencia de sepsis (61,5% en BGN multirresistentes vs. 46,6% en BGN, p = 0,011) y en la mortalidad a los 30 días (28,4 vs. 14,4%, p < 0,001). Sin embargo, no hubo diferencias significativas respecto a ingreso en UCI (19 vs. 19,4%, p = 0,936).
|
Características clínicas de los pacientes |
||||
|
Variable |
Total (n = 1.051) |
BGN (n = 971) |
BGNmr (n = 80) |
p |
|
Género (%) |
||||
|
Mujer |
42,2 |
42,7 |
36,3 |
0,259 |
|
Edad media (años) |
73,6 ± 15,2 |
73,3 ± 15,4 |
76,4 ± 12,7 |
0,087 |
|
Antecedentes (%) |
||||
|
Hipertensión arterial |
62,1 |
63,3 |
62 |
0,904 |
|
Dislipemia |
43,1 |
43 |
44,3 |
0,825 |
|
Diabetes mellitus |
35,3 |
35,3 |
35,4 |
0,974 |
|
Neumopatía crónica |
21,2 |
20,6 |
27,8 |
0,132 |
|
Enfermedad renal crónica |
15,8 |
15,6 |
19 |
0,425 |
|
Inmunosupresión (%) |
||||
|
Neoplasia de órgano sólido |
25,8 |
25,9 |
24,1 |
0,717 |
|
Neoplasia hematológica |
8,2 |
7,9 |
12,7 |
0,136 |
|
EAS |
5,3 |
5,2 |
6,3 |
0,657 |
|
Neutropenia < 500 cels/μL (%) |
6,2 |
6 |
9,1 |
0,277 |
|
Foco (%) |
||||
|
Urinario |
47,3 |
46,2 |
62,8 |
0,933 |
|
Abdominal |
29,2 |
30,3 |
16,5 |
0,009 |
|
Respiratorio |
4,5 |
4,4 |
6,3 |
0,415 |
|
Desconocido/Otros |
19 |
19,1 |
15,2 |
0,933 |
|
Microbiología (%) |
||||
|
Escherichia coli |
56,9 |
55,7 |
71,3 |
0,007 |
|
Klebsiella sp. |
18,6 |
19,8 |
5 |
< 0,001 |
|
Pseudomonas aeruginosa |
6,6 |
6,8 |
3,8 |
0,29 |
|
Enterobacter sp. |
3,8 |
3,9 |
2,5 |
0,525 |
|
Proteus mirabilis |
3,5 |
3,5 |
3,8 |
0,908 |
|
Otros |
21,6 |
11,5 |
13,8 |
< 0,001 |
|
IRAS (%) |
29,9 |
28,5 |
46,8 |
< 0,001 |
|
ATB 3 meses previos (%) |
35 |
32,3 |
67,1 |
< 0,001 |
|
Ingreso 3 meses previos (%) |
30,6 |
48,1 |
29,2 |
< 0,001 |
|
BGN: bacilo gram negativo; BGNmr: bacilo gram negativo multirresistente; EAS: enfermedades autoinmunes y sistémicas con tratamiento activo; IRAS: infecciones relacionadas con la asistencia sanitaria; ATB: antibioterapia. |
||||
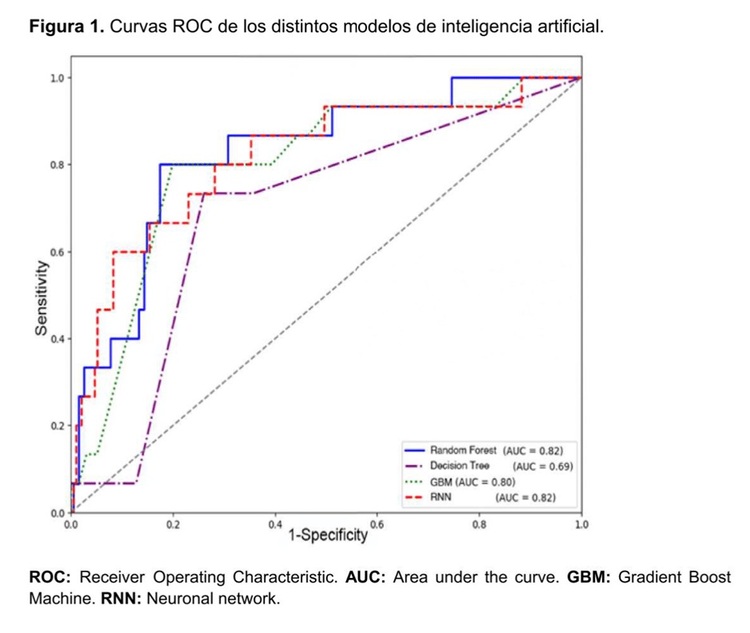
Discusión: La implementación de modelos de inteligencia artificial (IA) para predecir bacteriemias por bacilos Gram negativos multirresistentes ha demostrado un potencial significativo en nuestro estudio. La capacidad del modelo random forest para equilibrar precisión y sensibilidad, reflejada en los resultados obtenidos, subraya la viabilidad de aplicar técnicas de aprendizaje automático en entornos clínicos para predecir o establecer situaciones de alto riesgo de aparición de infecciones complejas. En particular, en el caso de bacteriemias por BGN multirresistentes, donde se observa un mayor riesgo de sepsis y mortalidad, es crucial poder predecir su presencia y realizar un manejo temprano para prevenir desenlaces adversos. La elección de random forest se justificó por su capacidad para manejar el desequilibrio de clases, un desafío común en estudios médicos donde los eventos de interés pueden ser minoritarios.
Conclusiones: Nuestro estudio demuestra el potencial de los modelos basados en IA, especialmente el modelo random forest, para mejorar la predicción y, potencialmente, el manejo de bacteriemias por bacilos Gram negativos multirresistentes.






